Bioinformatique. Emploi du temps, groupes de TP, supports de cours et de TP disponibles sur sur la page Enseignement
|
|
|
- Henri Chassé
- il y a 7 ans
- Total affichages :
Transcription
1 Bioinformatique Emploi du temps, groupes de TP, supports de cours et de TP disponibles sur sur la page Enseignement Contrôle continu : 30% Contrôle terminal : 70% Objectifs pédagogiques : Apperçu de quelques domaines d'application de la bioinformatique traitement d'image : mesures phénotypiques gestion des données statistiques : corrélation phénotype - génotype banques de données et sites Web publiques modélisation de systèmes biologiques et simulations Intervenants Roland Barriot Maxime Bonhomme Franck Delavoie Gwennaele Fichant Elodie Gaulin Florie Gosseau Silvia Kocanova
2 Définition 2 Qu'est-ce que la bioinformatique? Plusieurs réponses : pas de l'informatique bio traitement de l'information biologique un domaine spécialisé de la biologie un domaine de recherche multidiscpilinaire : biologie, santé, mathématique, informatique, physique, éthique Une définition : traitement des informations biologiques par des méthodes informatiques et/ou mathématiques. Les données et connaissances biologiques posent de nouveaux défis spécifiques pour leur gestion, représentation, et leur analyse/traitement
3 Historique et domaines d'application liés à la bioinformatique Apparition du terme bioinformatique Disponibilité de séquences de gènes (et du 1 er génome complet en 1977, bactériophage phi X174) Comparaison de séquences 1980 Alignement de séquences et recherche de séquences similaires Analyse phylogénétique Prédiction de fonction Banques de données 1990 Débuts de la génomique et génomique comparative ; analyse du contenu d'un génome Débuts des analyses globales de l'expression des gènes et des protéines Famille de gènes, de protéines, de domaines Prédiction de la structure 3D des protéines 2000 Généralisation des approches globales Traitement de graphes : interactions protéine-protéine, réseau de régulation de l'expression des gènes, réseau métaboliques Apprentissage automatique (data mining) Fouille de texte (text mining) Biologie des systèmes : modélisation de systèmes biologiques Intégration de données hétérogènes, visualisation Médecine personnalisée NGS/Séquençage très haut débit Traitement d'images liées à la microscopie 2010 Ethique, confidentialité des données Modélisation d'une cellule, d'un organisme, d'une population, d'un écosystème Biologie de synthèse
4 (Quelques) données et connaissances disponibles 4 métabolisme régulation Cytoplasme Noyau interactome chromosome génome protéome gaattcggccattcacatagc ctctacctccccctgccagtc ggctgggacaactcgggcaaa cccagctgagcttgagcg... transcription complexe protéique protéine ADN gène MTGLAEEWWFDSGRAA ARDWKKFTQALESRFT AMNMEEDWSNLQCGPN SYETRFRAARHHL... ARNm AGA CTATGT TGATACAG CTA traduction transcriptome Cellule eucaryote métabolome
5 Données omics 5 Génome séquence(s) nucléique(s) de l ensemble des chromosomes d un organisme ensemble des gènes d un organisme Transcriptome ensemble des ARNm ou transcrits présents dans une cellule ou une population de cellules dans des conditions données Protéome source : Wikipedia ensemble des protéines présentes dans une cellule ou une population de cellules dans des conditions données Interactome ensemble des intéractions moléculaires pouvant survenir in vivo ensemble des intéractions moléculaires dans des conditions données ensemble des intéractions au sein d un organisme : moléculaires, physiques, génétiques, fonctionnelles, Métabolome ensemble des métabolites présents dans une cellule ou une population de cellules dans des conditions données Exome, lipidome, phénome, régulome, sécrétome,
6 Séquences disponibles : quelques chiffres 6 June 2016
7 Des séquences et après? 7 Annotation régions prédiction codantes, régions régulatrice, fonctionnelle Reconstruction du réseau métabolique Analyse des relations génotype/phénotype Analyses évolutives Conception de puces d expression Identification de protéine Prédiction de structure
8 Assemblage d un génome 8 matériel biologique Sonication Sous-clonage et Séquençage ADN Génomique données Assemblage 1 Assemblage 2 Shotgun Contigs Séquence complète
9 L analyse manuelle d une séquence peut s avérer laborieuse 9 TCCTGGCCTACATGTTCTTTGGCAAAGGATCTTCAAAATCAACGGCTCCCGGTGCGGCGATCATCCATTTCTTCGGAGGGATT CACGAGATTTACTTCCCGTACATTCTGATGAAACCTGGCCCTGATTCTCGCAGCCATTGCCGGCGGAGCAAGCGGACTCTTA ACATTACGATCTTTAATGCCGGACTTGTCGCGGCAGCGTCACCGGGAAGCATTATCGCATTGATGGCAATGACGCCAAGAGG AGGCTATTTCGGCGTATTGGCGGGTGTATTGGTCGCTGCAGCTGTATCGTTCATCGTTTCAGCAGTGATCCTGAAATCCTCTA AAGCTAGTGAAGAAGACCTGGCTGCCGCAACAGAAAAAATGCAGTCCATGAAGGGGAAGAAAAGCCAAGCAGCAGCTGC TTTAGAGGCGGAACAAGCCAAAGCAGAGAAGCGTCTGAGCTGTCTCCTGAAAGCGCGAACAAAATTATCTTTTCGTGTGAT CCGGGATGGGATCAAGTGCCATGGGGGCATCCATCTTAAGAAACAAAGTGAAAAAGCGGAGCTTGACATCAGTGTGACCA ACACGGCCATTAACAATCTGCCAAGCGATGCGGATATTGTCATCACCCACAAAGATTTAACAGACCGCGCGAAAGCAAAGCT GCCGAACGCGACGCACATATCAGTGGATAACTTCTTAAACAGCCCGAAATACGACGAGCTGATTGAAAAGCTGAAAAGTAAT CTTATAGAAAGAGAGTATTGTCATGCAAGTACTCGCAAAGGAAACATTAAACTCAATCAAACGGTATCATCAAAAGAAGAGGC TATCAAATTGGCAGGCCAGACGCTGATTGACAACGGCTACGTGACAGAGGATTACATTAGCAAAATGTTTGACCGTGAAGAA ACGTCTTCTACGTTTATGGGGAATTTCATTGCCATTCCACACGGCACAGAAGAAGCGAAAAGCGAGGTGCTTCACTCAGGAA TTTCAATCATACAGATTCCAGAGGGCGTTGAGTACGGAGAAGGCAACACGGCAAAAGTGGTATTCGGCATTGCGGGTAAAA ATAATGAGCATTTAGACATTTTGTCTAACATCGCCATTATCTGTTCAGAAGAAGAAACATTGAACGCCTGATCTCCGCTAAAGC GAAGAAGATTTGATCGCCATTTCAACGAGGTGAACTGACATGATCGCCTTACATTTCGGTGCGGGAAATATCGGGAGAGGAT TTATCGGCGCGCTGCTTCACCACTCCGGCTATGATGTGGTGTTTGCGGATGTGAACGAAACGATGGTCAGCCTCCTCAATGA AAAAAAAGAATACACAGTGGAACTGGCGGAAGAGGGACGTTCATCGGAGATCATTGGCCCGGTGAGCGCTATTAACAGCG GCAGTCAGACCGAGGAGCTGTACCGGCTGATGAATGAGGCGGCGCTCATCACAACAGCTGTCGGCCCGAATGTCCTGAAG CTGATTGCCCCGTCTATCGCAGAAGGTTTAAGACGAAGAAATACTGCAAACACACTGAATATCATTGCCTGCGAAAATATGAT TGGCGGAAGCAGCTTCTTAAAGAAAGAAATATACAGCCATTTAACGGAAGCAGAGCAGAAATCCGTCAGTGAAACGTTAGG TTTTCCGAATTCTGCCGTTGACCGGATCGTCCCGATTCAGCATCATGAAGACCCGCTGAAAGTATCGGTTGAACCATTTTTCG AATGGGTCATTGATGAATCAGGCTTTAAAGGGAAAACACCAGTCATAAACGGCGCACTGTTTGTTGATGATTTAACGCCGTA CATCGAACGGAAGCTGTTTACGGTCAATACCGGACACGCGGTCACAGCGTATGTCGGCTATCAGCGCGGACTCAAAACGGT CAAAGAAGCAATTGATCATCCGGAAATCCGCCGTGTTGTTCATTCGGCGCTGCTTGAAACTGGTGACTATCTCGTCAAATCGT ATGGCTTTAAGCAAACTGAACACGAACAATATATTAAAAATCAGCGGTCGCTTTTAAAATCCTTTCATTTCGGACGATGTGACC CGCGTAGCGAGGTCACCTCTCAGAAAACTGGGAGAAAATGTAGACTTGTAGGCCCGGCAAAGAAAATAAAAGAACCGAAT GCACTGGCTGAAGGAATTGCCGCAGCACTGCGCTTCGATTTCACCGGTGACCCTGAAGCGGTTGAACTGCAAGCGCTGAT CGAAGAAAAGGATACAGCGGCGTACTTCAAGAGGTGTGCGGCATTCAGTCCCATGAACCGTTGCACGCCATCATTTTAAAG AAACTTAATCAATAACCGACCACCCGTGACACAATGTCACGGGCTTTTTACTATCTCGCAATCTAGTATAATAGAAAGCGCTTA CGATAACAGGGGAAGGAGAATGACGATGAAACAATTTGAGATTGCGGCAATACCGGGAGACGGAGTAGGAAAGAGGTTGT AGCGGCTGCTGAGAAAGTGCTTCATACAGCGGCTGAGGTACACGGAGGTTTGTCATTCTCATTCACAGCTTTTCCATGGAGC TGTGATTATTACTTGGAGCACGGCAAAAATGATGCCCGAAGATGGAATACATACGCTTACTCAATTTGAAGCAGTTTTTGGGA GCTGTCGGAAATCCGAAGCTGGTTCCCGATCATATATCGTTATGGGGCTGCTGCTGAAATCCGGAGGGAGCTTGAGCTTTCC
10 Annotation d un génome 10 Identification des gènes codant pour : les les les ARNr ARNt protéines Identification des unités de traduction Identification des unités de transcription (promoteur et terminateur) Pour les gènes codant pour les protéines, prédiction fonctionnelle par recherche de similarité de séquences (Blast) et classification en grandes classes fonctionnelles (ex: biosynthèse des acides aminés, métabolisme énergétique.)
11 Structure secondaire canonique d une séquence d ARNt 11 bras amino-acyl bras D bras T-Y-C boucle D boucle T-Y-C bras anticodon boucle variable boucle anticodon
12 Génome de Mycoplasma genitalium 12 Distribution des unités de traduction et classification fonctionnelle
13 Stockage des séquences : Banques de séquences 13 ID Q8DPI7_STRR6 PRELIMINARY; PRT; 286 AA. AC Q8DPI7; DT 01-MAR-2003, integrated into UniProtKB/TrEMBL. DT 01-MAR-2003, sequence version 1. DT 02-MAY-2006, entry version 10. DE DNA processing Smf protein. GN Name=smf; OrderedLocusNames=spr1144; OS Streptococcus pneumoniae (strain ATCC BAA-255 / R6). OC Bacteria; Firmicutes; Lactobacillales; Streptococcaceae; OC Streptococcus. OX NCBI_TaxID=171101; RN [1] RP NUCLEOTIDE SEQUENCE [LARGE SCALE GENOMIC DNA]. RX MEDLINE= ; PubMed= ; RX DOI= /JB ; RA Hoskins J., Alborn W.E. Jr., Arnold J., Blaszczak L.C., Burgett S., RA DeHoff B.S., Estrem S.T., Fritz L., Fu D.-J., Fuller W., Geringer C., RA Gilmour R., Glass J.S., Khoja H., Kraft A.R., Lagace R.E., RA LeBlanc D.J., Lee L.N., Lefkowitz E.J., Lu J., Matsushima P., RA McAhren S.M., McHenney M., McLeaster K., Mundy C.W., Nicas T.I., RA Norris F.H., O'Gara M., Peery R.B., Robertson G.T., Rockey P., RA Sun P.-M., Winkler M.E., Yang Y., Young-Bellido M., Zhao G., RA Zook C.A., Baltz R.H., Jaskunas S.R., Rosteck P.R. Jr., Skatrud P.L., RA Glass J.I.; RT "Genome of the bacterium Streptococcus pneumoniae strain R6."; RL J. Bacteriol. 183: (2001). CC CC Copyrighted by the UniProt Consortium, see CC Distributed under the Creative Commons Attribution-NoDerivs License CC DR EMBL; AE008487; AAK ; -; Genomic_DNA. DR PIR; A95147; A DR PIR; G98014; G DR GenomeReviews; AE007317_GR; spr1144. DR BioCyc; SPNE1313:SPR1144-MONOMER; -. DR GO; GO: ; P:DNA mediated transformation; IEA. DR InterPro; IPR003488; SMF. DR Pfam; PF02481; SMF; 1. DR TIGRFAMs; TIGR00732; dpra; 1. KW Complete proteome. SQ SEQUENCE 286 AA; MW; CF12DB83AE3663A2 CRC64; MELFMKITNY EIYKLKKSGL TNQQILKVLE YGENVDQELL LGDIADISGC RNPAVFMERY FQIDDAHLSK EFQKFPSFSI LDDCYPWDLS EIYDAPVLLF YKGNLDLLKF PKVAVVGSRA CSKQGAKSVE KVIQGLENEL VIVSGLAKGI DTAAHMAALQ NGGKTIAVIG TGLDVFYPKA NKRLQDYIGN DHLVLSEYGP GEQPLKFHFP ARNRIIAGLC RGVIVAEAKM RSGSLITCER AMEEGRDVFA IPGSILDGLS DGCHHLIQEG AKLVTSGQDV LAEFEF // Exemple d une entrée protéique dans la banque de données UniProt
14 Transcriptome 14 Transcriptome : ensemble des ARNm ou transcrits présents dans une population de cellules dans des conditions données. Accès au niveau d expression de milliers de gènes simultanément (potentiellement l ensemble des gènes d un organisme) = instantané de l état d une cellule ou d une population de cellules Données d expression des gènes obtenues par : qpcr Puces à ADN Séquençage ultra-haut débit
15 Acquisition des données (RNAseq) 15 Échantillon 1 Échantillon 2 ARNm extraction Traitement des données (assemblage, alignement sur le génome, normalisation ) Préparation de la librairie (sélection des fragments, ajout des linkers, ) ADNc séquençage (centaines de) millions de séquences (reads)
16 Transcriptome : acquisition des données 16 Échantillon test Échantillon référence ARNm extraction réverse transcription et amplification ADNc scan marquage + hybridation puis lavage
17 Transcriptome : analyse et interprétation des données 17 acquisition probesets mesures normalisation filtrage gènes conditions interprétation Identification des gènes différentiellement exprimés Identification des ensembles de gènes co-exprimés Caractérisation d un ensemble de gènes
18 Transcriptome : gènes co-exprimés 18 Motivation : les gènes ayant des profils d expression similaires sont potentiellement corégulés et participeraient donc à un même processus biologique But : regrouper les gènes impliqués dans un même processus biologique Robinson et al
19 Protéomique 19 Protéome : ensemble des protéines exprimées dans une cellule, une partie d'une cellule (membranes, organites) ou un groupe de cellules (organe, organisme, groupe d'organismes) dans des conditions données et à un moment donné. = instantané de l état d une cellule ou d une population de cellules Séparation des protéines par gels d électrophorèse (1D, 2D) puis identification des spots par spectrométrie de masse Échantillon test Échantillon référence
20 Protéomique : Identification de protéine 20 Digestion du spot par une enzyme (ex: trypsine) et mesure du poids des peptides obtenus Digestion in silico du protéome Recherche des protéines correspondant au profil observé
21 Réseaux de gènes et de protéines 21 Réseaux : d interactions protéine - protéine, génétiques, fonctionnelles, de régulation des gènes métabolisme (enzymes substrats) transduction du signal
22 Prédiction de structure 22 Séquence protéique >gi gb AAD cytochrome b LCLYTHIGRNIYYGSYLYSETWNTGIMLLLITMATAFMGYVLPWGQMSFWGATVITNLFSAIPYIGTNLV EWIWGGFSVDKATLNRFFAFHFILPFTMVALAGVHLTFLHETGSNNPLGLTSDSDKIPFHPYYTIKDFLG LLILILLLLLLALLSPDMLGDPDNHMPADPLNTPLHIKPEWYFLFAYAILRSVPNKLGGVLALFLSIVIL GLMPFLHTSKHRSMMLRPLSQALFWTLTMDLLTLTWIGSQPVEYPYTIIGQMASILYFSIILAFLPIAGX IENY Prédiction ou résolution de la structure tridimensionnelle
23 Biologie des systèmes 23 Intégration et synthèse des connaissances modélisation d un système processus biologique (respiration) organite (mitochondrie) cellule population écosystème À terme : simulation d une cellule virtuelle et prédiction de son comportement
24 Homologie et transfert d'annotation 24 ancêtre commun chromosome (ADN) spéciation Evolution = mutations organismes actuels ATPase similarité de séquences Du temps du séquençage des premiers gènes et génomes la conservation/similarité des séquences impliquait des fonctions similaires les annotations des gènes caractérisés expérimentalement étaient transférés aux nouveaux gènes/génomes séquencés
25 Homologie, orthologie et orthologie 1:1 25 Homologie : deux gènes sont homologues s'ils ont divergé à partir d'une même séquence ancêtre Paralogie définition : deux gènes sont paralogues si leur divergence a commencé après la duplication du gène ancêtre. hypothèse : mécanisme évolutif d'acquisition de nouvelles fonctions par accumulation de mutations sur une des deux "copies" du gène ancêtre non soumis à une pression de sélection? remarque : les deux gènes paralogues sont au départ dans le même génome. Orthologie définition : deux gènes sont ortholgues si leur divergence a commencé après un évènement de spéciation (le gène ancêtre se trouvait dans l'organisme ancêtre). remarque : deux gènes ortologues ne peuvent pas être présents dans le même génome. La relation d'orthologie est souvent abusivement utilisée pour déterminer la présence ou l'absence d'un gène dans un génome. Orthologie 1:1 définition : deux gènes orthologues sont orthologues 1:1 s'il n'y a pas eu de duplication (apparition de paralogue) après l'évènement de spéciation. remarque : la chronologie des évènements de spéciation et de duplication est importante. Deux orthologues 1:1 ont une forte probabilité d'avoir conservé la même fonction.
26 Chronologie des évènements 26 L'orthologie 1:1 est essentielle pour la prédiction de la fonction des gènes (par transfert d'annotations) Problèmes : la chronologie est nécessaire pour différencier paralogues, orthologues et orthologues 1:1 la chronologie n'est pas connue Deux principales approches pour identifier les orthologues 1:1 analyse et reconstruction de l'histoire évolutive représentation sous forme de graphe des relations d'orthologie
27 Prédiction des orthologues 1:1 27 Spéciation comparaisons de séquences Evolution = mutations Duplication Spéciation B B2 Duplication C C2 C22 A B B2 C C2 C22 comparaisons de toutes les séquences 2 à 2 B C prédit sim(b,c) > max(sim(b,b2), sim(c, C2), sim(c,c22)) B2 C22 non prédit sim(b2,c22) < sim(c2,c22) Remarque : calcul avec 7,223,104 séquences de génomes =>52, comparaisons
28 Autre évènement évolutif : perte de gènes 28 Spéciation comparaisons de séquences Duplication B B2 Spéciation Duplication perte pertes A B B2 C C2 C22 BBH C C2 C22 des séries de duplications et de pertes de gènes induisent des erreurs de prédiction
29 Transitivité de l'orthologie 1:1 29
30 Elagage des erreurs de prédiction 30 Méthodes de traitement de graphes Répresentation: sommets = gènes, liens = orthologues 1:1 Partitionnement de graphe = clustering = détection de communauté principe : les sommets très connectés entre eux sont isolés en cluster
31 Concepts et méthodes abordés dans cet UE 31
32 Traitements d'image 32
33 Bases de données 33
34 Banques et sites Web 34
35 Banques et sites Web 35 source
36 Modélisation de systèmes biologiques 36 Neidhardt et al Durzinsky et al., 2011
Master de Bioinformatique et Biologie des Systèmes Toulouse http://m2pbioinfo.biotoul.fr Responsable : Pr. Gwennaele Fichant
 Master de Bioinformatique et Biologie des Systèmes Toulouse http://m2pbioinfo.biotoul.fr Responsable : Pr. Gwennaele Fichant Parcours: Master 1 : Bioinformatique et biologie des Systèmes dans le Master
Master de Bioinformatique et Biologie des Systèmes Toulouse http://m2pbioinfo.biotoul.fr Responsable : Pr. Gwennaele Fichant Parcours: Master 1 : Bioinformatique et biologie des Systèmes dans le Master
MABioVis. Bio-informatique et la
 MABioVis Modèles et Algorithmes pour la Bio-informatique et la Visualisation Visite ENS Cachan 5 janvier 2011 MABioVis G GUY MELANÇON (PR UFR Maths Info / EPI GRAVITE) (là, maintenant) - MABioVis DAVID
MABioVis Modèles et Algorithmes pour la Bio-informatique et la Visualisation Visite ENS Cachan 5 janvier 2011 MABioVis G GUY MELANÇON (PR UFR Maths Info / EPI GRAVITE) (là, maintenant) - MABioVis DAVID
TD de Biochimie 4 : Coloration.
 TD de Biochimie 4 : Coloration. Synthèse de l expérience 2 Les questions posées durant l expérience 2 Exposé sur les méthodes de coloration des molécules : Générique Spécifique Autres Questions Pourquoi
TD de Biochimie 4 : Coloration. Synthèse de l expérience 2 Les questions posées durant l expérience 2 Exposé sur les méthodes de coloration des molécules : Générique Spécifique Autres Questions Pourquoi
CHAPITRE 3 LA SYNTHESE DES PROTEINES
 CHAITRE 3 LA SYNTHESE DES ROTEINES On sait qu un gène détient dans sa séquence nucléotidique, l information permettant la synthèse d un polypeptide. Ce dernier caractérisé par sa séquence d acides aminés
CHAITRE 3 LA SYNTHESE DES ROTEINES On sait qu un gène détient dans sa séquence nucléotidique, l information permettant la synthèse d un polypeptide. Ce dernier caractérisé par sa séquence d acides aminés
La gestion de données dans le cadre d une application de recherche d alignement de séquence : BLAST.
 La gestion de données dans le cadre d une application de recherche d alignement de séquence : BLAST. Gaël Le Mahec - p. 1/12 L algorithme BLAST. Basic Local Alignment Search Tool est un algorithme de recherche
La gestion de données dans le cadre d une application de recherche d alignement de séquence : BLAST. Gaël Le Mahec - p. 1/12 L algorithme BLAST. Basic Local Alignment Search Tool est un algorithme de recherche
Dr E. CHEVRET UE2.1 2013-2014. Aperçu général sur l architecture et les fonctions cellulaires
 Aperçu général sur l architecture et les fonctions cellulaires I. Introduction II. Les microscopes 1. Le microscope optique 2. Le microscope à fluorescence 3. Le microscope confocal 4. Le microscope électronique
Aperçu général sur l architecture et les fonctions cellulaires I. Introduction II. Les microscopes 1. Le microscope optique 2. Le microscope à fluorescence 3. Le microscope confocal 4. Le microscope électronique
Biomarqueurs en Cancérologie
 Biomarqueurs en Cancérologie Définition, détermination, usage Biomarqueurs et Cancer: définition Anomalie(s) quantitative(s) ou qualitative(s) Indicative(s) ou caractéristique(s) d un cancer ou de certaines
Biomarqueurs en Cancérologie Définition, détermination, usage Biomarqueurs et Cancer: définition Anomalie(s) quantitative(s) ou qualitative(s) Indicative(s) ou caractéristique(s) d un cancer ou de certaines
Bibliographie Introduction à la bioinformatique
 Bibliographie Introduction à la bioinformatique 5. Les bases de données biologiques, SQL et la programmation Python/C++ Zvelebil et Baum, Understanding bioinformatics Beighley, Head First SQL Chari, A
Bibliographie Introduction à la bioinformatique 5. Les bases de données biologiques, SQL et la programmation Python/C++ Zvelebil et Baum, Understanding bioinformatics Beighley, Head First SQL Chari, A
Big data et sciences du Vivant L'exemple du séquençage haut débit
 Big data et sciences du Vivant L'exemple du séquençage haut débit C. Gaspin, C. Hoede, C. Klopp, D. Laborie, J. Mariette, C. Noirot, MS. Trotard bioinfo@genopole.toulouse.inra.fr INRA - MIAT - Plate-forme
Big data et sciences du Vivant L'exemple du séquençage haut débit C. Gaspin, C. Hoede, C. Klopp, D. Laborie, J. Mariette, C. Noirot, MS. Trotard bioinfo@genopole.toulouse.inra.fr INRA - MIAT - Plate-forme
DÉFIS DU SÉQUENÇAGE NOUVELLE GÉNÉRATION
 DÉFIS DU SÉQUENÇAGE NOUVELLE GÉNÉRATION PRINCIPES DE BASE SUR LES DONNEES ET LE CALCUL HAUTE PERFORMANCE Lois de Gray sur l ingénierie des données 1 : Les calculs scientifiques traitent des volumes considérables
DÉFIS DU SÉQUENÇAGE NOUVELLE GÉNÉRATION PRINCIPES DE BASE SUR LES DONNEES ET LE CALCUL HAUTE PERFORMANCE Lois de Gray sur l ingénierie des données 1 : Les calculs scientifiques traitent des volumes considérables
Génétique et génomique Pierre Martin
 Génétique et génomique Pierre Martin Principe de la sélections Repérage des animaux intéressants X Accouplements Programmés Sélection des meilleurs mâles pour la diffusion Index diffusés Indexation simultanée
Génétique et génomique Pierre Martin Principe de la sélections Repérage des animaux intéressants X Accouplements Programmés Sélection des meilleurs mâles pour la diffusion Index diffusés Indexation simultanée
Environmental Research and Innovation ( ERIN )
 DÉpartEment RDI Environmental Research and Innovation ( ERIN ) Le département «Environmental Research and Innovation» (ERIN) du LIST élabore des stratégies, des technologies et des outils visant à mieux
DÉpartEment RDI Environmental Research and Innovation ( ERIN ) Le département «Environmental Research and Innovation» (ERIN) du LIST élabore des stratégies, des technologies et des outils visant à mieux
Introduction aux bases de données: application en biologie
 Introduction aux bases de données: application en biologie D. Puthier 1 1 ERM206/Technologies Avancées pour le Génome et la Clinique, http://tagc.univ-mrs.fr/staff/puthier, puthier@tagc.univ-mrs.fr ESIL,
Introduction aux bases de données: application en biologie D. Puthier 1 1 ERM206/Technologies Avancées pour le Génome et la Clinique, http://tagc.univ-mrs.fr/staff/puthier, puthier@tagc.univ-mrs.fr ESIL,
Les OGM. 5 décembre 2008. Nicole Mounier
 Les OGM 5 décembre 2008 Nicole Mounier Université Claude Bernard Lyon 1 CGMC, bâtiment Gregor Mendel 43, boulevard du 11 Novembre 1918 69622 Villeurbanne Cedex OGM Organismes Génétiquement Modifiés Transfert
Les OGM 5 décembre 2008 Nicole Mounier Université Claude Bernard Lyon 1 CGMC, bâtiment Gregor Mendel 43, boulevard du 11 Novembre 1918 69622 Villeurbanne Cedex OGM Organismes Génétiquement Modifiés Transfert
GénoToul 2010, Hôtel de Région Midi Pyrénées, Toulouse, 10 décembre 2010
 GénoToul 2010, Hôtel de Région Midi Pyrénées, Toulouse, 10 décembre 2010 Analyse de la diversité moléculaire des régions génomiques de 30 gènes du développement méristématique dans une core collection
GénoToul 2010, Hôtel de Région Midi Pyrénées, Toulouse, 10 décembre 2010 Analyse de la diversité moléculaire des régions génomiques de 30 gènes du développement méristématique dans une core collection
e-biogenouest CNRS UMR 6074 IRISA-INRIA / Plateforme de Bioinformatique GenOuest yvan.le_bras@irisa.fr Programme fédérateur Biogenouest co-financé
 e-biogenouest Coordinateur : Olivier Collin Animateur : Yvan Le Bras CNRS UMR 6074 IRISA-INRIA / Plateforme de Bioinformatique GenOuest yvan.le_bras@irisa.fr Programme fédérateur Biogenouest co-financé
e-biogenouest Coordinateur : Olivier Collin Animateur : Yvan Le Bras CNRS UMR 6074 IRISA-INRIA / Plateforme de Bioinformatique GenOuest yvan.le_bras@irisa.fr Programme fédérateur Biogenouest co-financé
! Séquence et structure des macromolécules. " Séquences protéiques (UniProt) " Séquences nucléotidiques (EMBL / ENA, Genbank, DDBJ)
 Introduction à la Bioinformatique Introduction! Les bases de données jouent un rôle crucial dans l organisation des connaissances biologiques.! Nous proposons ici un tour rapide des principales bases de
Introduction à la Bioinformatique Introduction! Les bases de données jouent un rôle crucial dans l organisation des connaissances biologiques.! Nous proposons ici un tour rapide des principales bases de
Mise en place d une plateforme de gestion de matériels biologiques : quels avantages pour les chercheurs?
 Mise en place d une plateforme de gestion de matériels biologiques : quels avantages pour les chercheurs? Dr Xavier Manival, Laboratoire IMoPA, CR, CNRS Françoise Tisserand-Bedri, Documentaliste, Inist-CNRS
Mise en place d une plateforme de gestion de matériels biologiques : quels avantages pour les chercheurs? Dr Xavier Manival, Laboratoire IMoPA, CR, CNRS Françoise Tisserand-Bedri, Documentaliste, Inist-CNRS
ULBI 101 Biologie Cellulaire L1. Le Système Membranaire Interne
 ULBI 101 Biologie Cellulaire L1 Le Système Membranaire Interne De la nécessité d un SMI Le volume augmente comme le cube de la dimension linéaire, alors que la surface n'est augmentée que du carré Une
ULBI 101 Biologie Cellulaire L1 Le Système Membranaire Interne De la nécessité d un SMI Le volume augmente comme le cube de la dimension linéaire, alors que la surface n'est augmentée que du carré Une
Semestre 2 Spécialité «Analyse in silico des complexes macromolécules biologiques-médicaments»
 Master In silico Drug Design Semestre 2 Spécialité «Analyse in silico des complexes macromolécules biologiques-médicaments» 30NU01IS INITIATION A LA PROGRAMMATION (6 ECTS) Responsables : D. MESTIVIER,
Master In silico Drug Design Semestre 2 Spécialité «Analyse in silico des complexes macromolécules biologiques-médicaments» 30NU01IS INITIATION A LA PROGRAMMATION (6 ECTS) Responsables : D. MESTIVIER,
Base de données bibliographiques Pubmed-Medline
 Chapitre 1 ; Domaine 1 ; Documentation ; Champs référentiels 1.1.1, 1.1.2 et 1.1.3 Base de données bibliographiques Pubmed-Medline D r Patrick Deschamps,, 30 mai 2007 PLAN C2i métiers de la santé Introduction
Chapitre 1 ; Domaine 1 ; Documentation ; Champs référentiels 1.1.1, 1.1.2 et 1.1.3 Base de données bibliographiques Pubmed-Medline D r Patrick Deschamps,, 30 mai 2007 PLAN C2i métiers de la santé Introduction
IMMUNOLOGIE. La spécificité des immunoglobulines et des récepteurs T. Informations scientifiques
 IMMUNOLOGIE La spécificité des immunoglobulines et des récepteurs T Informations scientifiques L infection par le VIH entraîne des réactions immunitaires de l organisme qui se traduisent par la production
IMMUNOLOGIE La spécificité des immunoglobulines et des récepteurs T Informations scientifiques L infection par le VIH entraîne des réactions immunitaires de l organisme qui se traduisent par la production
UTILISATION DE LA PLATEFORME WEB D ANALYSE DE DONNÉES GALAXY
 UTILISATION DE LA PLATEFORME WEB D ANALYSE DE DONNÉES GALAXY Yvan Le Bras yvan.le_bras@irisa.fr Cyril Monjeaud, Mathieu Bahin, Claudia Hériveau, Olivier Quenez, Olivier Sallou, Aurélien Roult, Olivier
UTILISATION DE LA PLATEFORME WEB D ANALYSE DE DONNÉES GALAXY Yvan Le Bras yvan.le_bras@irisa.fr Cyril Monjeaud, Mathieu Bahin, Claudia Hériveau, Olivier Quenez, Olivier Sallou, Aurélien Roult, Olivier
Comment reproduire les résultats de l article : POP-Java : Parallélisme et distribution orienté objet
 Comment reproduire les résultats de l article : POP-Java : Parallélisme et distribution orienté objet Beat Wolf 1, Pierre Kuonen 1, Thomas Dandekar 2 1 icosys, Haute École Spécialisée de Suisse occidentale,
Comment reproduire les résultats de l article : POP-Java : Parallélisme et distribution orienté objet Beat Wolf 1, Pierre Kuonen 1, Thomas Dandekar 2 1 icosys, Haute École Spécialisée de Suisse occidentale,
Eco-système calcul et données
 Eco-système calcul et données M. Daydé Dr du Comité d'orientation pour le Calcul Intensif (COCIN) Délégué Scientifique INS2I en charge HPC / Grille / Cloud Calcul / données : un enjeu stratégique Calcul
Eco-système calcul et données M. Daydé Dr du Comité d'orientation pour le Calcul Intensif (COCIN) Délégué Scientifique INS2I en charge HPC / Grille / Cloud Calcul / données : un enjeu stratégique Calcul
Chapitre 7 : Structure de la cellule Le noyau cellulaire
 UE2 : Structure générale de la cellule Chapitre 7 : Structure de la cellule Le noyau cellulaire Professeur Michel SEVE Année universitaire 2010/2011 Université Joseph Fourier de Grenoble - Tous droits
UE2 : Structure générale de la cellule Chapitre 7 : Structure de la cellule Le noyau cellulaire Professeur Michel SEVE Année universitaire 2010/2011 Université Joseph Fourier de Grenoble - Tous droits
Mise en place d une solution automatique de stockage et de visualisation de données de capture des interactions chromatiniennes à l échelle génomique
 Rapport de stage de deuxième année de DUT Génie Biologique option Bioinformatique Mise en place d une solution automatique de stockage et de visualisation de données de capture des interactions chromatiniennes
Rapport de stage de deuxième année de DUT Génie Biologique option Bioinformatique Mise en place d une solution automatique de stockage et de visualisation de données de capture des interactions chromatiniennes
De la physico-chimie à la radiobiologie: nouveaux acquis (I)
 De la physico-chimie à la radiobiologie: nouveaux acquis (I) Collaboration: - Laboratoire de Radiotoxicologie et Oncologie (L. Sabatier) CEA, DSV - Laboratoire de Génotoxicité et Modulation de l Expression
De la physico-chimie à la radiobiologie: nouveaux acquis (I) Collaboration: - Laboratoire de Radiotoxicologie et Oncologie (L. Sabatier) CEA, DSV - Laboratoire de Génotoxicité et Modulation de l Expression
CATALOGUE DES PRESTATIONS DE LA
 1/23 La plate-forme Biopuces et Séquençage de Strasbourg est équipée des technologies Affymetrix et Agilent pour l étude du transcriptome et du génome sur puces à ADN. SOMMAIRE ANALYSE TRANSCRIPTIONNELLE...
1/23 La plate-forme Biopuces et Séquençage de Strasbourg est équipée des technologies Affymetrix et Agilent pour l étude du transcriptome et du génome sur puces à ADN. SOMMAIRE ANALYSE TRANSCRIPTIONNELLE...
E-BIOGENOUEST, VERS UN ENVIRONNEMENT VIRTUEL DE RECHERCHE (VRE) ORIENTÉ SCIENCES DE LA VIE? Intervenant(s) : Yvan Le Bras, Olivier Collin
 E-BIOGENOUEST, VERS UN ENVIRONNEMENT VIRTUEL DE RECHERCHE (VRE) ORIENTÉ SCIENCES DE LA VIE? Intervenant(s) : Yvan Le Bras, Olivier Collin E-BIOGENOUEST Programme fédérateur Biogenouest co-financé par les
E-BIOGENOUEST, VERS UN ENVIRONNEMENT VIRTUEL DE RECHERCHE (VRE) ORIENTÉ SCIENCES DE LA VIE? Intervenant(s) : Yvan Le Bras, Olivier Collin E-BIOGENOUEST Programme fédérateur Biogenouest co-financé par les
Séquence 2. L expression du patrimoine génétique. Sommaire
 Séquence 2 L expression du patrimoine génétique Sommaire 1. La synthèse des protéines 2. Phénotypes, génotypes et environnement Synthèse de la séquence 2 Exercices de la séquence 2 Glossaire des séquences
Séquence 2 L expression du patrimoine génétique Sommaire 1. La synthèse des protéines 2. Phénotypes, génotypes et environnement Synthèse de la séquence 2 Exercices de la séquence 2 Glossaire des séquences
Cellules procaryotes Service histologie Pr.k.mebarek
 Cellules procaryotes Service histologie Pr.k.mebarek I) Les cellules procaryotes II) Les cellules eucaryotes o 1) Caractéristiques générales des cellules eucaryotes o 2) Organisation des cellules eucaryotes
Cellules procaryotes Service histologie Pr.k.mebarek I) Les cellules procaryotes II) Les cellules eucaryotes o 1) Caractéristiques générales des cellules eucaryotes o 2) Organisation des cellules eucaryotes
présentée DEVANT L UNIVERSITÉ DE RENNES 1 pour obtenir le grade de : DOCTEUR DE L UNIVERSITÉ DE RENNES 1 PAR Emilie GUÉRIN TITRE DE LA THÈSE :
 N Ordre de la Thèse 3282 THÈSE présentée DEVANT L UNIVERSITÉ DE RENNES 1 pour obtenir le grade de : DOCTEUR DE L UNIVERSITÉ DE RENNES 1 Mention : BIOLOGIE PAR Emilie GUÉRIN Équipe d accueil : École Doctorale
N Ordre de la Thèse 3282 THÈSE présentée DEVANT L UNIVERSITÉ DE RENNES 1 pour obtenir le grade de : DOCTEUR DE L UNIVERSITÉ DE RENNES 1 Mention : BIOLOGIE PAR Emilie GUÉRIN Équipe d accueil : École Doctorale
Détection et prise en charge de la résistance aux antirétroviraux
 Détection et prise en charge de la résistance aux antirétroviraux Jean Ruelle, PhD AIDS Reference Laboratory, UCLouvain, Bruxelles Corata 2011, Namur, 10 juin 2011 Laboratoires de référence SIDA (Belgique)
Détection et prise en charge de la résistance aux antirétroviraux Jean Ruelle, PhD AIDS Reference Laboratory, UCLouvain, Bruxelles Corata 2011, Namur, 10 juin 2011 Laboratoires de référence SIDA (Belgique)
Identification de nouveaux membres dans des familles d'interleukines
 Identification de nouveaux membres dans des familles d'interleukines Nicolas Beaume Jérôme Mickolajczak Gérard Ramstein Yannick Jacques 1ère partie : Définition de la problématique Les familles de gènes
Identification de nouveaux membres dans des familles d'interleukines Nicolas Beaume Jérôme Mickolajczak Gérard Ramstein Yannick Jacques 1ère partie : Définition de la problématique Les familles de gènes
Introduc)on à Ensembl/ Biomart : Par)e pra)que
 Introduc)on à Ensembl/ Biomart : Par)e pra)que Stéphanie Le Gras Jean Muller NAVIGUER DANS ENSEMBL : PARTIE PRATIQUE 2 Naviga)on dans Ensembl : Pra)que Exercice 1 1.a. Quelle est la version de l assemblage
Introduc)on à Ensembl/ Biomart : Par)e pra)que Stéphanie Le Gras Jean Muller NAVIGUER DANS ENSEMBL : PARTIE PRATIQUE 2 Naviga)on dans Ensembl : Pra)que Exercice 1 1.a. Quelle est la version de l assemblage
Physiopathologie : de la Molécule à l'homme
 Mention Sciences du Vivant Spécialité de Master : Physiopathologie : de la Molécule à l'homme Pourquoi, comment, combien, contourner, greffer, restaurer, inhiber, suppléer Responsables : Dr Gilles Prévost
Mention Sciences du Vivant Spécialité de Master : Physiopathologie : de la Molécule à l'homme Pourquoi, comment, combien, contourner, greffer, restaurer, inhiber, suppléer Responsables : Dr Gilles Prévost
LA MITOSE CUEEP - USTL DÉPARTEMENT SCIENCES BAHIJA DELATTRE
 Biologie LA MITOSE CUEEP - USTL DÉPARTEMENT SCIENCES BAHIJA DELATTRE Février 2006 I. L'INTRODUCTION Chaque cellule d'un organisme supérieur provient de la multiplication d'une cellule préexistante (cellule
Biologie LA MITOSE CUEEP - USTL DÉPARTEMENT SCIENCES BAHIJA DELATTRE Février 2006 I. L'INTRODUCTION Chaque cellule d'un organisme supérieur provient de la multiplication d'une cellule préexistante (cellule
Université d Evry-Val d Essonne Ecole Doctorale des Génomes Aux Organismes. Thèse
 Université d Evry-Val d Essonne Ecole Doctorale des Génomes Aux Organismes Thèse Présentée pour obtenir le grade de Docteur en sciences de l université d Evry-Val d Essonne Spécialité Bioinformatique par
Université d Evry-Val d Essonne Ecole Doctorale des Génomes Aux Organismes Thèse Présentée pour obtenir le grade de Docteur en sciences de l université d Evry-Val d Essonne Spécialité Bioinformatique par
Gènes Diffusion - EPIC 2010
 Gènes Diffusion - EPIC 2010 1. Contexte. 2. Notion de génétique animale. 3. Profil de l équipe plateforme. 4. Type et gestion des données biologiques. 5. Environnement Matériel et Logiciel. 6. Analyses
Gènes Diffusion - EPIC 2010 1. Contexte. 2. Notion de génétique animale. 3. Profil de l équipe plateforme. 4. Type et gestion des données biologiques. 5. Environnement Matériel et Logiciel. 6. Analyses
Hépatite chronique B Moyens thérapeutiques
 Hépatite chronique B Moyens thérapeutiques Dr Olfa BAHRI Laboratoire de Virologie Clinique Institut Pasteur de Tunis INTRODUCTION Plus de 300. 10 6 porteurs chroniques de VHB dans le monde Hépatite chronique
Hépatite chronique B Moyens thérapeutiques Dr Olfa BAHRI Laboratoire de Virologie Clinique Institut Pasteur de Tunis INTRODUCTION Plus de 300. 10 6 porteurs chroniques de VHB dans le monde Hépatite chronique
MASTER (LMD) MANAGEMENT DE PROJET ET INNOVATION EN BIOTECHNOLOGIE
 MASTER (LMD) MANAGEMENT DE PROJET ET INNOVATION EN BIOTECHNOLOGIE RÉSUMÉ DE LA FORMATION Type de diplôme : Master (LMD) Domaine ministériel : Sciences, Technologies, Santé Mention : BIOLOGIE SANTE Spécialité
MASTER (LMD) MANAGEMENT DE PROJET ET INNOVATION EN BIOTECHNOLOGIE RÉSUMÉ DE LA FORMATION Type de diplôme : Master (LMD) Domaine ministériel : Sciences, Technologies, Santé Mention : BIOLOGIE SANTE Spécialité
SysFera. Benjamin Depardon
 SysFera Passage d applications en SaaS Benjamin Depardon CTO@SysFera SysFera Technologie 2001 Création 2010 Spin Off INRIA Direction par un consortium d investisseurs 12 personnes 75% en R&D Implantation
SysFera Passage d applications en SaaS Benjamin Depardon CTO@SysFera SysFera Technologie 2001 Création 2010 Spin Off INRIA Direction par un consortium d investisseurs 12 personnes 75% en R&D Implantation
Les débuts de la génétique
 HPITRE 9 DES DÉBTS DE L ÉNÉTIQE X ENJEX TELS DES BIOTEHNOLOIES 1 Les débuts de la génétique est avec les travaux de regor Mendel vers la fin du XIX e siècle que furent posées les bases de la génétique.
HPITRE 9 DES DÉBTS DE L ÉNÉTIQE X ENJEX TELS DES BIOTEHNOLOIES 1 Les débuts de la génétique est avec les travaux de regor Mendel vers la fin du XIX e siècle que furent posées les bases de la génétique.
Mise en œuvre de la virtualisation à l IGBMC. Guillaume Seith Remy Fritz
 Mise en œuvre de la virtualisation à l IGBMC. Guillaume Seith Remy Fritz Introduction Contexte Objectifs Mise en œuvre Présentation Exploitation Conclusion IGBMC: Institut de génétique et de Biologie Moléculaire
Mise en œuvre de la virtualisation à l IGBMC. Guillaume Seith Remy Fritz Introduction Contexte Objectifs Mise en œuvre Présentation Exploitation Conclusion IGBMC: Institut de génétique et de Biologie Moléculaire
Formavie 2010. 2 Différentes versions du format PDB...3. 3 Les champs dans les fichiers PDB...4. 4 Le champ «ATOM»...5. 6 Limites du format PDB...
 Formavie 2010 Les fichiers PDB Les fichiers PDB contiennent les informations qui vont permettre à des logiciels de visualisation moléculaire (ex : RasTop ou Jmol) d afficher les molécules. Un fichier au
Formavie 2010 Les fichiers PDB Les fichiers PDB contiennent les informations qui vont permettre à des logiciels de visualisation moléculaire (ex : RasTop ou Jmol) d afficher les molécules. Un fichier au
Journée SITG, Genève 15 octobre 2013. Nicolas Lachance-Bernard M.ATDR Doctorant, Laboratoire de systèmes d information géographique
 Monitorint spatio-temporel intégré de la mobilité urbaine Monitoring spatio-temporel de l ADN urbain Une réponse aux défis, problèmes, enjeux et risques des milieux urbains Nicolas Lachance-Bernard M.ATDR
Monitorint spatio-temporel intégré de la mobilité urbaine Monitoring spatio-temporel de l ADN urbain Une réponse aux défis, problèmes, enjeux et risques des milieux urbains Nicolas Lachance-Bernard M.ATDR
Analyse des données de séquençage massif par des méthodes phylogénétiques
 Analyse des données de séquençage massif par des méthodes phylogénétiques Roux S., Taib N., Mangot J.F., Hugoni M., Mary I., Ravet V., Bronner G., Enault F., Debroas D. Équipe Microbiologie de l'environnement
Analyse des données de séquençage massif par des méthodes phylogénétiques Roux S., Taib N., Mangot J.F., Hugoni M., Mary I., Ravet V., Bronner G., Enault F., Debroas D. Équipe Microbiologie de l'environnement
Spécialisation 3A AgroSup Dijon IAA Microbiologie Industrielle et Biotechnologie (MIB)
 Spécialisation 3A AgroSup Dijon IAA Microbiologie Industrielle et Biotechnologie (MIB) Responsable : Jean-François Cavin (Pr. Microbiologie Biotechnologie) Tel 03 80 77 40 72, Fax 03 80 77 23 84 jf.cavin@agrosupdijon.fr
Spécialisation 3A AgroSup Dijon IAA Microbiologie Industrielle et Biotechnologie (MIB) Responsable : Jean-François Cavin (Pr. Microbiologie Biotechnologie) Tel 03 80 77 40 72, Fax 03 80 77 23 84 jf.cavin@agrosupdijon.fr
Stages - le calendrier
 Stages - le calendrier BIOCHIMIE ET BIOTECHNOLOGIES Ingénieurs pluridisciplinaires formés en chimie, biochimie analytique et fonctionnelle, biologie cellulaire et moléculaire, microbiologie, physiologie
Stages - le calendrier BIOCHIMIE ET BIOTECHNOLOGIES Ingénieurs pluridisciplinaires formés en chimie, biochimie analytique et fonctionnelle, biologie cellulaire et moléculaire, microbiologie, physiologie
Introduction à la Génomique Fonctionnelle
 Introduction à la Génomique Fonctionnelle Cours aux étudiants de BSc Biologie 3ème année Philippe Reymond, MER PLAN DU COURS - Séquençage des génomes - Fabrication de DNA microarrays - Autres méthodes
Introduction à la Génomique Fonctionnelle Cours aux étudiants de BSc Biologie 3ème année Philippe Reymond, MER PLAN DU COURS - Séquençage des génomes - Fabrication de DNA microarrays - Autres méthodes
Détection des duplications en tandem au niveau nucléique à l'aide de la théorie des flots
 Université Toulouse 3 Paul Sabatier(UT3 Paul Sabatier) Informatique Spécialité Bioinformatique Eric AUDEMARD lundi 28 novembre 2011 Détection des duplications en tandem au niveau nucléique à l'aide de
Université Toulouse 3 Paul Sabatier(UT3 Paul Sabatier) Informatique Spécialité Bioinformatique Eric AUDEMARD lundi 28 novembre 2011 Détection des duplications en tandem au niveau nucléique à l'aide de
Bases de données des mutations
 Bases de données des mutations CFMDB CFTR2 CFTR-France / Registre Corinne THEZE, Corinne BAREIL Laboratoire de génétique moléculaire Montpellier Atelier Muco, Lille, 25-27 septembre 2014 Accès libre http://www.genet.sickkids.on.ca/app
Bases de données des mutations CFMDB CFTR2 CFTR-France / Registre Corinne THEZE, Corinne BAREIL Laboratoire de génétique moléculaire Montpellier Atelier Muco, Lille, 25-27 septembre 2014 Accès libre http://www.genet.sickkids.on.ca/app
Big Data: développement, rôle des ARS?? Laurent Tréluyer, ARS Ile de France Alain Livartowski Institut Curie Paris 01/12/2014
 Big Data: développement, rôle des ARS?? Laurent Tréluyer, ARS Ile de France Alain Livartowski Institut Curie Paris 01/12/2014 1 Classiquement, le Big Data se définit autour des 3 V : Volume, Variété et
Big Data: développement, rôle des ARS?? Laurent Tréluyer, ARS Ile de France Alain Livartowski Institut Curie Paris 01/12/2014 1 Classiquement, le Big Data se définit autour des 3 V : Volume, Variété et
Performances. Gestion des serveurs (2/2) Clustering. Grid Computing
 Présentation d Oracle 10g Chapitre VII Présentation d ORACLE 10g 7.1 Nouvelles fonctionnalités 7.2 Architecture d Oracle 10g 7.3 Outils annexes 7.4 Conclusions 7.1 Nouvelles fonctionnalités Gestion des
Présentation d Oracle 10g Chapitre VII Présentation d ORACLE 10g 7.1 Nouvelles fonctionnalités 7.2 Architecture d Oracle 10g 7.3 Outils annexes 7.4 Conclusions 7.1 Nouvelles fonctionnalités Gestion des
2D-Differential Differential Gel Electrophoresis & Applications en neurosciences
 2D-Differential Differential Gel Electrophoresis & Applications en neurosciences Jean-Etienne Poirrier Centre de Neurobiologie Cellulaire et Moléculaire Centre de Recherches du Cyclotron Université de
2D-Differential Differential Gel Electrophoresis & Applications en neurosciences Jean-Etienne Poirrier Centre de Neurobiologie Cellulaire et Moléculaire Centre de Recherches du Cyclotron Université de
EMME : un environnement de gestion des métadonnées expérimentales
 EMME : un environnement de gestion des métadonnées expérimentales Basé sur l'utilisation d'isa Infrastructure Cyril Monjeaud Ingénieur sur la plate-forme GenOuest, Rennes PLAN Introduction ISA Infrastructure
EMME : un environnement de gestion des métadonnées expérimentales Basé sur l'utilisation d'isa Infrastructure Cyril Monjeaud Ingénieur sur la plate-forme GenOuest, Rennes PLAN Introduction ISA Infrastructure
Perl Orienté Objet BioPerl There is more than one way to do it
 Perl Orienté Objet BioPerl There is more than one way to do it Bérénice Batut, berenice.batut@udamail.fr DUT Génie Biologique Option Bioinformatique Année 2014-2015 Perl Orienté Objet - BioPerl Rappels
Perl Orienté Objet BioPerl There is more than one way to do it Bérénice Batut, berenice.batut@udamail.fr DUT Génie Biologique Option Bioinformatique Année 2014-2015 Perl Orienté Objet - BioPerl Rappels
UE6 - Cycle de vie du médicament : Conception rationnelle
 UE6 - Cycle de vie du médicament : Conception rationnelle Dr. Raphaël Terreux Faculté de Pharmacie (ISPB) Département pédagogique des Sciences Physico-Chimiques et Pharmacie Galénique 8 avenue Rockefeller,
UE6 - Cycle de vie du médicament : Conception rationnelle Dr. Raphaël Terreux Faculté de Pharmacie (ISPB) Département pédagogique des Sciences Physico-Chimiques et Pharmacie Galénique 8 avenue Rockefeller,
Les bases de données transcriptionnelles en ligne
 Les bases de données transcriptionnelles en ligne Différents concepts en régulation transcriptionnelle sites de fixation - in vitro/vivo? - quelle technique? - degré de confiance? facteur de transcription
Les bases de données transcriptionnelles en ligne Différents concepts en régulation transcriptionnelle sites de fixation - in vitro/vivo? - quelle technique? - degré de confiance? facteur de transcription
Ingénieur R&D en bio-informatique
 Ingénieur R&D en bio-informatique Spécialisé Bases De Données 33 ans, Célibataire. Biologie & Informatique gabriel.chandesris[at]laposte.net {06 56 41 97 37} Use the bipper! http://gabriel.chandesris.free.fr/
Ingénieur R&D en bio-informatique Spécialisé Bases De Données 33 ans, Célibataire. Biologie & Informatique gabriel.chandesris[at]laposte.net {06 56 41 97 37} Use the bipper! http://gabriel.chandesris.free.fr/
MAB Solut. vos projets. MABLife Génopole Campus 1 5 rue Henri Desbruères 91030 Evry Cedex. www.mabsolut.com. intervient à chaque étape de
 Mabsolut-DEF-HI:Mise en page 1 17/11/11 17:45 Page1 le département prestataire de services de MABLife de la conception à la validation MAB Solut intervient à chaque étape de vos projets Création d anticorps
Mabsolut-DEF-HI:Mise en page 1 17/11/11 17:45 Page1 le département prestataire de services de MABLife de la conception à la validation MAB Solut intervient à chaque étape de vos projets Création d anticorps
VI- Expression du génome
 VI- Expression du génome VI-1.- EXPRESSION DU GÉNOME- PRINCIPES GÉNÉRAUX DOGME CENTRAL Les gènes et l information génétique sont conservés sous forme d acides nucléiques La perpétuation à l identique de
VI- Expression du génome VI-1.- EXPRESSION DU GÉNOME- PRINCIPES GÉNÉRAUX DOGME CENTRAL Les gènes et l information génétique sont conservés sous forme d acides nucléiques La perpétuation à l identique de
Contrôle de l'expression génétique : Les régulations post-transcriptionnelles
 Contrôle de l'expression génétique : Les régulations post-transcriptionnelles http://perso.univ-rennes1.fr/serge.hardy/ utilisateur : biochimie mot de passe : 2007 L'ARNm, simple intermédiaire entre le
Contrôle de l'expression génétique : Les régulations post-transcriptionnelles http://perso.univ-rennes1.fr/serge.hardy/ utilisateur : biochimie mot de passe : 2007 L'ARNm, simple intermédiaire entre le
Contrôle de l'expression génétique :
 Contrôle de l'expression génétique : Les régulations post-transcriptionnelles L'ARNm, simple intermédiaire entre le génome et les protéines? gène protéine L'ARNm, simple intermédiaire entre le génome et
Contrôle de l'expression génétique : Les régulations post-transcriptionnelles L'ARNm, simple intermédiaire entre le génome et les protéines? gène protéine L'ARNm, simple intermédiaire entre le génome et
Présentation de l entreprise :
 Catalogue des stages 2014 1 Table des matières Présentation de l entreprise :... 3 Titre : Application pour le suivi des sportifs... 4 Titre : Mise en place d un module de «mobilisation client»... 4 Titre
Catalogue des stages 2014 1 Table des matières Présentation de l entreprise :... 3 Titre : Application pour le suivi des sportifs... 4 Titre : Mise en place d un module de «mobilisation client»... 4 Titre
Univers Vivant Révision. Notions STE
 Univers Vivant Révision Notions STE Chap. 13) L Écologie 1) a) Qu est-ce que l empreinte écologique? L empreinte écologique correspond à la surface terrestre et aquatique totale nécessaire à un individu,
Univers Vivant Révision Notions STE Chap. 13) L Écologie 1) a) Qu est-ce que l empreinte écologique? L empreinte écologique correspond à la surface terrestre et aquatique totale nécessaire à un individu,
Présentation du Master Ingénierie Informatique et du Master Science Informatique 2007-2008, Année 2 Université Paris-Est Marne-la-Vallée
 Présentation du Master Ingénierie Informatique et du Master Science Informatique 2007-2008, Année 2 Université Paris-Est Marne-la-Vallée Responsable du Master Informatique : Marc Zipstein Responsable de
Présentation du Master Ingénierie Informatique et du Master Science Informatique 2007-2008, Année 2 Université Paris-Est Marne-la-Vallée Responsable du Master Informatique : Marc Zipstein Responsable de
LES BIOTECHNOLOGIES DANS LE DIAGNOSTIC DES MALADIES INFECTIEUSES ET LE DÉVELOPPEMENT DES VACCINS
 CHAPITRE 1.1.7. LES BIOTECHNOLOGIES DANS LE DIAGNOSTIC DES MALADIES INFECTIEUSES ET LE DÉVELOPPEMENT DES VACCINS INTRODUCTION Les méthodes de biologie moléculaire ont de plus en plus d applications dans
CHAPITRE 1.1.7. LES BIOTECHNOLOGIES DANS LE DIAGNOSTIC DES MALADIES INFECTIEUSES ET LE DÉVELOPPEMENT DES VACCINS INTRODUCTION Les méthodes de biologie moléculaire ont de plus en plus d applications dans
Génomique Comparative et intégrative
 Génomique Comparative et intégrative Introduction : Le big data : on peut traiter des données massives à présent, l'objectif à présent est d'éviter les transferts de données trop longs. On a tout à portée
Génomique Comparative et intégrative Introduction : Le big data : on peut traiter des données massives à présent, l'objectif à présent est d'éviter les transferts de données trop longs. On a tout à portée
Rôle des acides biliaires dans la régulation de l homéostasie du glucose : implication de FXR dans la cellule bêta-pancréatique
 Rôle des acides biliaires dans la régulation de l homéostasie du glucose : implication de FXR dans la cellule bêta-pancréatique Tuteur : Anne Muhr-Tailleux cardiovasculaires et diabète (Equipe 1) Institut
Rôle des acides biliaires dans la régulation de l homéostasie du glucose : implication de FXR dans la cellule bêta-pancréatique Tuteur : Anne Muhr-Tailleux cardiovasculaires et diabète (Equipe 1) Institut
Module Analyse de Génomes 2011-2012 Master 2 module FMBS 326 Immunoinformatique
 Module Analyse de Génomes 2011-2012 Master 2 module FMBS 326 Immunoinformatique Planning du Module : Date Heure Salle 12/12 9h-12h TD info TA1Z bat 25 13h-17h TD info TA1Z bat 25 13/12 9h-12h TD info TA1Z
Module Analyse de Génomes 2011-2012 Master 2 module FMBS 326 Immunoinformatique Planning du Module : Date Heure Salle 12/12 9h-12h TD info TA1Z bat 25 13h-17h TD info TA1Z bat 25 13/12 9h-12h TD info TA1Z
GMIN206 Info. Biologique et Outils bioinformatiques. Elodie Cassan
 M Bioinformatique, Connaissances et Données Année 24-25 GMIN206 Info. Biologique et Outils bioinformatiques Banques de données biologiques (3h de Cours +,5h de TD + 4h de TP) Elodie Cassan Anne-Muriel
M Bioinformatique, Connaissances et Données Année 24-25 GMIN206 Info. Biologique et Outils bioinformatiques Banques de données biologiques (3h de Cours +,5h de TD + 4h de TP) Elodie Cassan Anne-Muriel
Séquence 6. Mais ces espèces pour autant ne sont pas identiques et parfois d ailleurs ne se ressemblent pas vraiment.
 Sommaire Séquence 6 Nous avons vu dans les séances précédentes qu au cours des temps géologiques des espèces différentes se sont succédé, leur apparition et leur disparition étant le résultat de modifications
Sommaire Séquence 6 Nous avons vu dans les séances précédentes qu au cours des temps géologiques des espèces différentes se sont succédé, leur apparition et leur disparition étant le résultat de modifications
Hémochromatose génétique non liée à HFE-1 : quand et comment la rechercher? Cécilia Landman 11 décembre 2010
 Hémochromatose génétique non liée à HFE-1 : quand et comment la rechercher? Cécilia Landman 11 décembre 2010 Métabolisme du fer : hepcidine Fer absorbé par les entérocytes des villosités duodénales : transporteur
Hémochromatose génétique non liée à HFE-1 : quand et comment la rechercher? Cécilia Landman 11 décembre 2010 Métabolisme du fer : hepcidine Fer absorbé par les entérocytes des villosités duodénales : transporteur
4 : MÉTHODES D ANALYSE UTILISÉES EN ÉCOLOGIE MICROBIENNE
 4 : MÉTHODES D ANALYSE UTILISÉES EN ÉCOLOGIE MICROBIENNE L écologie microbienne (ou étude des micro-organismes de l environnement) étudie : les relations entre les différentes populations de micro-organismes
4 : MÉTHODES D ANALYSE UTILISÉES EN ÉCOLOGIE MICROBIENNE L écologie microbienne (ou étude des micro-organismes de l environnement) étudie : les relations entre les différentes populations de micro-organismes
Objectifs. Clustering. Principe. Applications. Applications. Cartes de crédits. Remarques. Biologie, Génomique
 Objectifs Clustering On ne sait pas ce qu on veut trouver : on laisse l algorithme nous proposer un modèle. On pense qu il existe des similarités entre les exemples. Qui se ressemble s assemble p. /55
Objectifs Clustering On ne sait pas ce qu on veut trouver : on laisse l algorithme nous proposer un modèle. On pense qu il existe des similarités entre les exemples. Qui se ressemble s assemble p. /55
Biologie Appliquée. Dosages Immunologiques TD9 Mai 2015. Stéphanie Sigaut INSERM U1141 stephanie.sigaut@inserm.fr
 Biologie Appliquée Dosages Immunologiques TD9 Mai 2015 Stéphanie Sigaut INSERM U1141 stephanie.sigaut@inserm.fr 1 ELISA 2 3 4 [Ac] 5 6 7 8 9 Correction : Faire la moyenne D0-1 et D0-2 pour toute les valeurs
Biologie Appliquée Dosages Immunologiques TD9 Mai 2015 Stéphanie Sigaut INSERM U1141 stephanie.sigaut@inserm.fr 1 ELISA 2 3 4 [Ac] 5 6 7 8 9 Correction : Faire la moyenne D0-1 et D0-2 pour toute les valeurs
Biochimie I. Extraction et quantification de l hexokinase dans Saccharomyces cerevisiae 1. Assistants : Tatjana Schwabe Marcy Taylor Gisèle Dewhurst
 Biochimie I Extraction et quantification de l hexokinase dans Saccharomyces cerevisiae 1 Daniel Abegg Sarah Bayat Alexandra Belfanti Assistants : Tatjana Schwabe Marcy Taylor Gisèle Dewhurst Laboratoire
Biochimie I Extraction et quantification de l hexokinase dans Saccharomyces cerevisiae 1 Daniel Abegg Sarah Bayat Alexandra Belfanti Assistants : Tatjana Schwabe Marcy Taylor Gisèle Dewhurst Laboratoire
Rapport Scientifique Seine-Aval 3
 Rapport Scientifique Seine-Aval 3 Séminaire Seine-Aval 2008 Fiches de synthèse des propositions SA4 THEME 3 : TABLEAU DE BORD ET INDICATEURS OPERATIONNELS PUCES A ADN CHEZ MYTILUS EDULIS - 2005 - Danger
Rapport Scientifique Seine-Aval 3 Séminaire Seine-Aval 2008 Fiches de synthèse des propositions SA4 THEME 3 : TABLEAU DE BORD ET INDICATEURS OPERATIONNELS PUCES A ADN CHEZ MYTILUS EDULIS - 2005 - Danger
Service de collaboration en ligne. Microsoft Office 365
 Service de collaboration en ligne Microsoft Office 365 Produits inclus Valeurs ajoutés Ensemble complet des produits de productivité de Microsoft Référence du marché! Accès universel Peu importe où l utilisateur
Service de collaboration en ligne Microsoft Office 365 Produits inclus Valeurs ajoutés Ensemble complet des produits de productivité de Microsoft Référence du marché! Accès universel Peu importe où l utilisateur
Plateforme. DArT (Diversity Array Technology) Pierre Mournet
 Plateforme DArT (Diversity Array Technology) Pierre Mournet Lundi 8 avril 203 Pourquoi des DArT? Développement rapide et peu onéreux de marqueurs : Pas d information de séquence nécessaire. Pas de pré-requis
Plateforme DArT (Diversity Array Technology) Pierre Mournet Lundi 8 avril 203 Pourquoi des DArT? Développement rapide et peu onéreux de marqueurs : Pas d information de séquence nécessaire. Pas de pré-requis
Possibilités offertes après la L2?
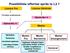 Possibilités offertes après la L2? Licence Pro Licence Générale Formation professionnel Diplôme Bac +3 Diplôme Bac +3 Master Vie Active : Technicien Assistant Ingénieur Laboratoire Public et Privé Master
Possibilités offertes après la L2? Licence Pro Licence Générale Formation professionnel Diplôme Bac +3 Diplôme Bac +3 Master Vie Active : Technicien Assistant Ingénieur Laboratoire Public et Privé Master
ELUCIDATION OF THE METABOLIC NETWORK TOPOLOGY IN METHYLOBACTERIUM EXTORQUENS AM1 AND ITS OPERATION UNDER PURE AND MIXED SUBSTRATE CONDITIONS
 Diss. ETH N 19955 ELUCIDATION OF THE METABOLIC NETWORK TOPOLOGY IN METHYLOBACTERIUM EXTORQUENS AM1 AND ITS OPERATION UNDER PURE AND MIXED SUBSTRATE CONDITIONS DISSERTATION Submitted to ETH ZURICH For the
Diss. ETH N 19955 ELUCIDATION OF THE METABOLIC NETWORK TOPOLOGY IN METHYLOBACTERIUM EXTORQUENS AM1 AND ITS OPERATION UNDER PURE AND MIXED SUBSTRATE CONDITIONS DISSERTATION Submitted to ETH ZURICH For the
Luca : à la recherche du plus proche ancêtre commun universel Patrick Forterre, Simonetta Gribaldo, Céline Brochier
 MEDECINE/SCIENCES 2005 ; 21 :???-??? > L application des méthodes de la biologie moléculaire à l étude des premières étapes de l évolution a montré que le monde vivant pouvait être divisé en trois domaines
MEDECINE/SCIENCES 2005 ; 21 :???-??? > L application des méthodes de la biologie moléculaire à l étude des premières étapes de l évolution a montré que le monde vivant pouvait être divisé en trois domaines
OBJECTIFS. Une démarche E-science
 E-BIOGENOUEST Programme fédérateur Biogenouest co-financé par les Régions Bretagne et Pays de la Loire 24 mois Lancé depuis Mai 2012 Porteur : Olivier Collin (IRISA) Animateur : Yvan Le Bras (IRISA) OBJECTIFS
E-BIOGENOUEST Programme fédérateur Biogenouest co-financé par les Régions Bretagne et Pays de la Loire 24 mois Lancé depuis Mai 2012 Porteur : Olivier Collin (IRISA) Animateur : Yvan Le Bras (IRISA) OBJECTIFS
La PCR quantitative (qpcr) et le guide de bonnes pratiques MIQE : adaptation et pertinence dans le contexte de la biologie clinique
 Synthèse Ann Biol Clin 2014 ; 72 (3) : 265-9 La PCR quantitative (qpcr) et le guide de bonnes pratiques MIQE : adaptation et pertinence dans le contexte de la biologie clinique Quantitative PCR (qpcr)
Synthèse Ann Biol Clin 2014 ; 72 (3) : 265-9 La PCR quantitative (qpcr) et le guide de bonnes pratiques MIQE : adaptation et pertinence dans le contexte de la biologie clinique Quantitative PCR (qpcr)
L équipement informatique pour le module EECA. Kit d enregistrement (KE) Description des pré-requis techniques et de configuration minimale
 M AT E R IEL L OG ICIEL D OC UM E N T AT ION 1 L équipement informatique pour le module EECA Kit d enregistrement (KE) Description des pré-requis techniques et de configuration minimale 1. Composition
M AT E R IEL L OG ICIEL D OC UM E N T AT ION 1 L équipement informatique pour le module EECA Kit d enregistrement (KE) Description des pré-requis techniques et de configuration minimale 1. Composition
Big Data et la santé
 Big Data, c'est quoi? Big Data et la santé Collecte, stockage et exploitation de masses de données Capter de façon automatique et anonyme une très grande quantité d'informations, les traiter avec des algorithmes
Big Data, c'est quoi? Big Data et la santé Collecte, stockage et exploitation de masses de données Capter de façon automatique et anonyme une très grande quantité d'informations, les traiter avec des algorithmes
Segmentation d'images à l'aide d'agents sociaux : applications GPU
 Segmentation d'images à l'aide d'agents sociaux : applications GPU Richard MOUSSA Laboratoire Bordelais de Recherche en Informatique (LaBRI) - UMR 5800 Université de Bordeaux - France Laboratoire de recherche
Segmentation d'images à l'aide d'agents sociaux : applications GPU Richard MOUSSA Laboratoire Bordelais de Recherche en Informatique (LaBRI) - UMR 5800 Université de Bordeaux - France Laboratoire de recherche
Circuits RL et RC. Chapitre 5. 5.1 Inductance
 Chapitre 5 Circuits RL et RC Ce chapitre présente les deux autres éléments linéaires des circuits électriques : l inductance et la capacitance. On verra le comportement de ces deux éléments, et ensuite
Chapitre 5 Circuits RL et RC Ce chapitre présente les deux autres éléments linéaires des circuits électriques : l inductance et la capacitance. On verra le comportement de ces deux éléments, et ensuite
Information génétique
 chapitre 3 Information génétique et division cellulaire L étude de la division cellulaire est abordée pour découvrir comment est transmise et conservée l information génétique portée par les chromosomes.
chapitre 3 Information génétique et division cellulaire L étude de la division cellulaire est abordée pour découvrir comment est transmise et conservée l information génétique portée par les chromosomes.
Limitations of the Playstation 3 for High Performance Cluster Computing
 Introduction Plan Limitations of the Playstation 3 for High Performance Cluster Computing July 2007 Introduction Plan Introduction Intérêts de la PS3 : rapide et puissante bon marché L utiliser pour faire
Introduction Plan Limitations of the Playstation 3 for High Performance Cluster Computing July 2007 Introduction Plan Introduction Intérêts de la PS3 : rapide et puissante bon marché L utiliser pour faire
www.gbo.com/bioscience 1 Culture Cellulaire Microplaques 2 HTS- 3 Immunologie/ HLA 4 Microbiologie/ Bactériologie Containers 5 Tubes/ 6 Pipetage
 2 HTS 3 Immunologie / Immunologie Informations Techniques 3 I 2 ELISA 96 Puits 3 I 4 ELISA 96 Puits en Barrettes 3 I 6 en Barrettes de 8 Puits 3 I 7 en Barrettes de 12 Puits 3 I 8 en Barrettes de 16 Puits
2 HTS 3 Immunologie / Immunologie Informations Techniques 3 I 2 ELISA 96 Puits 3 I 4 ELISA 96 Puits en Barrettes 3 I 6 en Barrettes de 8 Puits 3 I 7 en Barrettes de 12 Puits 3 I 8 en Barrettes de 16 Puits
Protéomique Séance 1 Introduction aux données de protéomique et aux outils de recherche
 Protéomique Séance 1 Introduction aux données de protéomique et aux outils de recherche Mathieu Courcelles BCM2003 26 Mars 2009 BCM2003-H09 Protéomique Démonstrateur: Mathieu Courcelles Questions? Via
Protéomique Séance 1 Introduction aux données de protéomique et aux outils de recherche Mathieu Courcelles BCM2003 26 Mars 2009 BCM2003-H09 Protéomique Démonstrateur: Mathieu Courcelles Questions? Via
EXERCICES : MECANISMES DE L IMMUNITE : pages 406 407 408 409 410
 EXERCICES : MECANISMES DE L IMMUNITE : pages 406 407 408 409 410 EXERCICE 1 PAGE 406 : EXPERIENCES A INTERPRETER Question : rôles respectifs du thymus et de la moelle osseuse dans la production des lymphocytes.
EXERCICES : MECANISMES DE L IMMUNITE : pages 406 407 408 409 410 EXERCICE 1 PAGE 406 : EXPERIENCES A INTERPRETER Question : rôles respectifs du thymus et de la moelle osseuse dans la production des lymphocytes.
Introduction, présentation de la plateforme South Green. h"p://southgreen.cirad.fr/
 Introduction, présentation de la plateforme South Green. h"p://southgreen.cirad.fr/ SupAgro, Montpellier, 10 février 2014 Le déluge de données NGS Next-generation sequencing Rappel: synthèse de l ADN 5
Introduction, présentation de la plateforme South Green. h"p://southgreen.cirad.fr/ SupAgro, Montpellier, 10 février 2014 Le déluge de données NGS Next-generation sequencing Rappel: synthèse de l ADN 5
Laboratoire de Photophysique et de Photochimie Supra- et Macromoléculaires (UMR 8531)
 Unité Mixte du CNRS (UMR8531) Institut de Chimie Directeur : Keitaro NAKATANI (PU ENS Cachan) Courrier électronique : nakatani@ppsm.ens-cachan.fr http://www.ppsm.ens-cachan.fr Problématique générale :
Unité Mixte du CNRS (UMR8531) Institut de Chimie Directeur : Keitaro NAKATANI (PU ENS Cachan) Courrier électronique : nakatani@ppsm.ens-cachan.fr http://www.ppsm.ens-cachan.fr Problématique générale :
Séquence 4. La nature du vivant. Sommaire. 1. L unité structurale et chimique du vivant. 2. L ADN, support de l information génétique
 Séquence 4 La nature du vivant Sommaire 1. L unité structurale et chimique du vivant 2. L ADN, support de l information génétique 3. Synthèse de la séquence 4. Exercices Devoir autocorrectif n 2 Séquence
Séquence 4 La nature du vivant Sommaire 1. L unité structurale et chimique du vivant 2. L ADN, support de l information génétique 3. Synthèse de la séquence 4. Exercices Devoir autocorrectif n 2 Séquence
PROJET MASTERS. Spécialités de master : analyse de l existant. Clusters. Cluster Acronymes Spécialités Effectif
 Spécialités de master : analyse de l existant Clusters A AAIS MAS Astronomie, astrophysique et ingénierie spatiale Mécanique, Aéronautique, Spatial 36 DSME Dimensionnement des systèmes mécaniques dans
Spécialités de master : analyse de l existant Clusters A AAIS MAS Astronomie, astrophysique et ingénierie spatiale Mécanique, Aéronautique, Spatial 36 DSME Dimensionnement des systèmes mécaniques dans
